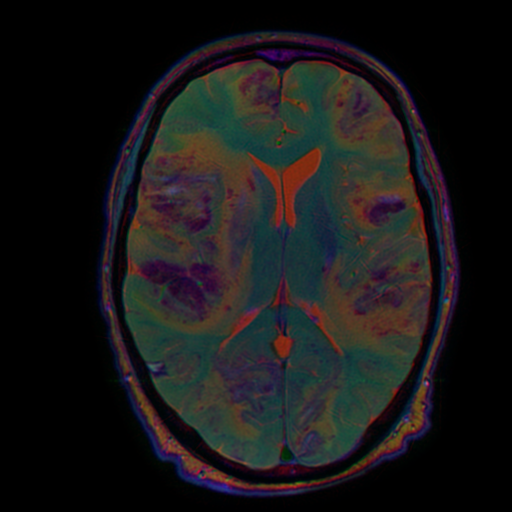
Когда мы работаем с задачей классификации или сегментации каких-то МРТ-данных, то сталкиваемся с тем, что серии с разной взвешенностью нарезаны в разных плоскостях и с разной толщиной среза. Это можно исправить.
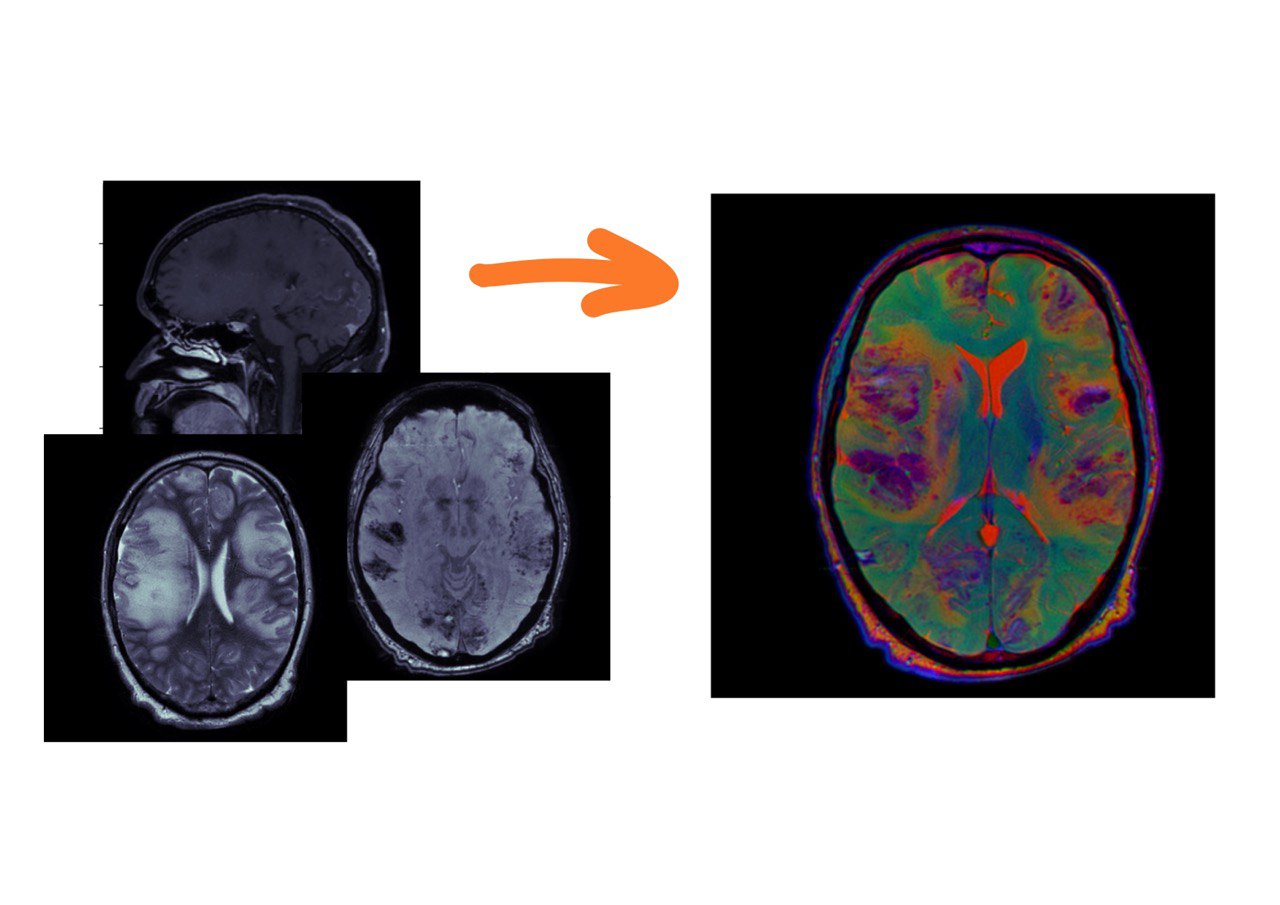
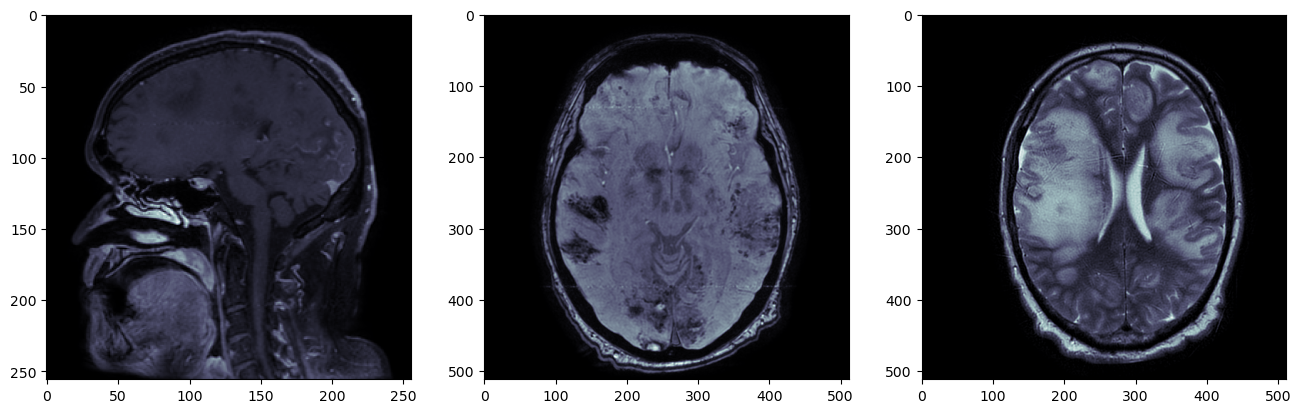
Для наглядности я взял T1 с контрастным усилением, SWI и T2. Т1-взвешенная серия нарезана сагиттально, SWI и Т2 – аксиально.
import os
import glob
import pydicom
import numpy as np
import nibabel as nib
from PIL import Image
import SimpleITK as sitk
import matplotlib.pyplot as plt
resample_dir = '.'
glob.glob(f'{resample_dir}/**')
>> ['. \\\\\\mri_resampling.ipynb',
'. \\\\\\SWI',
'. \\\\\\T1_CE',
'. \\\\\\T2']
fig, axs = plt.subplots(nrows=1, ncols=3, figsize=(16,6))
axs[0].imshow(pydicom.dcmread(f'{resample_dir}/T1_CE/IMG-0003-00140.dcm').pixel_array, cmap='bone')
axs[1].imshow(pydicom.dcmread(f'{resample_dir}/SWI/IMG-0005-00046.dcm').pixel_array, cmap='bone')
axs[2].imshow(pydicom.dcmread(f'{resample_dir}/T2/IMG-0002-00030.dcm').pixel_array, cmap='bone')
Каждая из этих серий содержит полезную информацию, и мы хотим показывать нейросетке все три взвешенности. Для этого их нужно подавать как каналы (примерно так, как делал фотографии Прокудин-Горский в начале 20 века: делал три фотографии через разные светофильтры, а потом накладывал их друг на друга).

1. (не слишком важный раздел) Матрица аффинной трансформации и простой ресемплинг 🔗
Каждый DICOM-файл хранит информацию о его ориентации в пространстве томографа (которое, в сущности, является частью реального мира с центром координатной сетки в изоцентре МРТ).
Давайте сконвертируем одну из томографических серий в NIfTI-файл, чтобы это стало наиболее наглядно.
reader = sitk.ImageSeriesReader()
reader.LoadPrivateTagsOn()
filenamesDICOM = reader.GetGDCMSeriesFileNames('T2')
reader.SetFileNames(filenamesDICOM)
t2_sitk = reader.Execute()
sitk.WriteImage(t2_sitk,'t2.nii')
После конвертации в NIfTI можно открыть этот файл с помощью библиотеки Nibabel. В ее объекте nibabel.nifti1.Nifti1Image много всего интересного, но две главных составляющих - воксельный массив и матрица аффинного преобразования.
t2_nib = nib.load('t2.nii')
t2_nib_array = t2_nib.get_fdata() #воксельный массив
t2_nib_array.shape
>> (512, 512, 48) - такая размерность у массива
plt.imshow(t2_nib_array[:,:,t2_nib_array.shape[2]//2], cmap='gray')
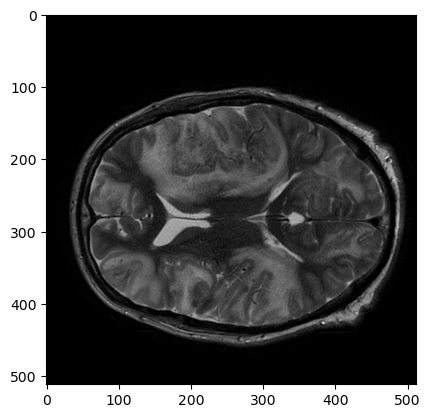
Это воксельный массив. Его расположение в пространстве томографа представлено в матрице аффинного преобразования:
np.set_printoptions(precision=4, suppress=True)
t2_nib.affine
>> array([[ -0.4222, -0.0167, 0.5434, 99.3905],
[ 0.0131, -0.429 , -0.149 , 143.058 ],
[ 0.0785, -0.0186, 2.9466, -60.64 ],
[ 0. , 0. , 0. , 1. ]])
Левая верхняя часть 3х3 содержит информацию о повороте и масштабе. Четвертая колонка отражает смещение относительно центра магнита.
Таким образом, если мы хотим узнать координаты вокселя с индексом [2,5,10] в пространстве томографа, мы можем просто посчитать скалярное произведение левой верхней части матрицы размера 3х3 и поэлементно сложить результат с вектором смещения t (т.е. с четвертым столбцом).
$$ 1) \begin{bmatrix} A_{ 00 } & A_{ 01 } & A_{ 02 } \\\ A_{ 10 } & A_{ 11 } & A_{ 12 } \\\ A_{ 20 } & A_{ 21 } & A_{ 22 }\end{bmatrix} \cdot \begin{bmatrix} { b_0 } \\\ { b_1 } \\\ { b_2 } \end{bmatrix} = \begin{bmatrix} A_{ 00 } \\\ A_{ 10 } \\\ A_{ 20 } \end{bmatrix} \cdot { b_0 } + \begin{bmatrix} A_{ 01 } \\\ A_{ 11 } \\\ A_{ 21 } \end{bmatrix} \cdot { b_1 } + \begin{bmatrix} A_{ 02 } \\\ A_{ 12 } \\\ A_{ 22 } \end{bmatrix} \cdot { b_2 } = \begin{bmatrix} A_{ 00 } { b_0 } + A_{ 01 } { b_1 } + A_{ 02 } { b_2 } \\\ A_{ 10 } { b_0 } + A_{ 11 } { b_1 } + A_{ 12 } { b_2 } \\\ A_{ 20 } { b_0 } + A_{ 21 } { b_1 } + A_{ 22 } { b_2 } \end{bmatrix} = \begin{bmatrix} { x_0 } \\\ { x_1 } \\\ { x_2 } \end{bmatrix} $$
$$ 2) \begin{bmatrix} { x_0 } \\\ { x_1 } \\\ { x_2 } \end{bmatrix} + \begin{bmatrix} { t_0 } \\\ { t_1 } \\\ { t_2 } \end{bmatrix} = \begin{bmatrix} { x_0+t_0 } \\\ { x_1+t_1 } \\\ { x_2+t_2 } \end{bmatrix} = \begin{bmatrix} a \\\ { b } \\\ { c } \end{bmatrix} $$
t2_nib.affine[:3,:3] @ np.array([2,5,10]) + t2_nib.affine[:3,3]
>>array([103.89633372, 139.44894546, -31.10983373])
Последняя строка матрицы аффиного преобразования в дикомах всегда [0,0,0,1], как в единичной матрице. Это нужно просто для того, чтобы сделать матрицу квадратной, тогда ее можно будет использовать как линейный оператор.
t2_nib.affine @ np.array([2,5,10,1]) #(просто добавили единицу как четвертую координату)
>> array([103.89633372, 139.44894546, -31.10983373, 1. ])
Очевидно, все отдельно взятые сканы головного мозга в пределах одного исследования привязаны к пространству томогрфа, а значит можно их ресемплировать в общее воксельное пространство.
filenamesDICOM = reader.GetGDCMSeriesFileNames('T1_CE')
reader.SetFileNames(filenamesDICOM)
t1_sitk = reader.Execute()
sitk.WriteImage(t1_sitk,'t1.nii')
t1_nib = nib.load('t1.nii')
t1_nib_array = t1_nib.get_fdata()
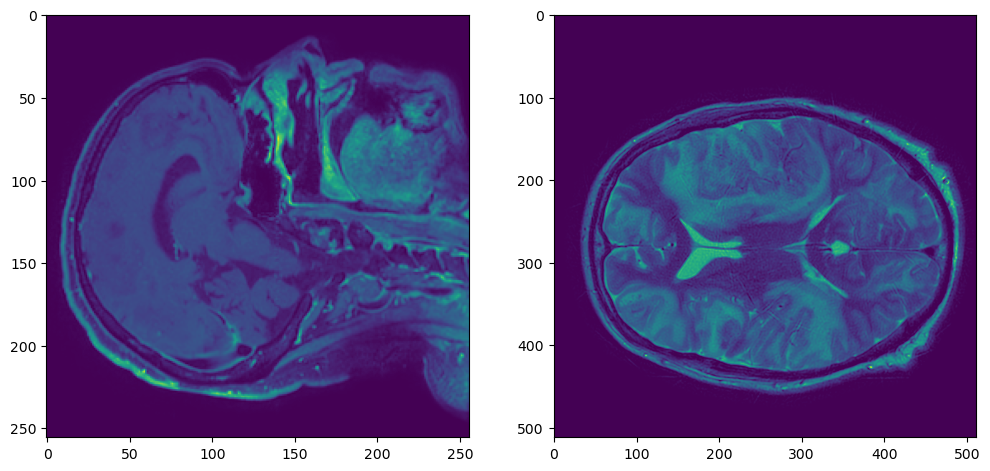
plt.figure(figsize=(12,6))
plt.subplot(121)
plt.imshow(t1_nib_array[:,:,t1_nib_array.shape[2]//2])
plt.subplot(122)
plt.imshow(t2_nib_array[:,:,t2_nib_array.shape[2]//2])
Давайте воспользуемся для этого готовой функцией resample_img из библиотеки nilearn.
from nilearn.image import resample_img
%%time
t1_resampled = resample_img(t1_nib, target_affine=t2_nib.affine, target_shape=t2_nib.shape)
t1_resampled_array = t1_resampled.get_fdata()
>> CPU times: total: 13.6 s
Wall time: 14.6 s
plt.figure(figsize=(12,6))
plt.subplot(121)
plt.imshow(t2_nib_array[:,:,t2_nib_array.shape[2]//2])
plt.subplot(122)
plt.imshow(t1_resampled_array[:,:,t1_resampled_array.shape[2]//2])
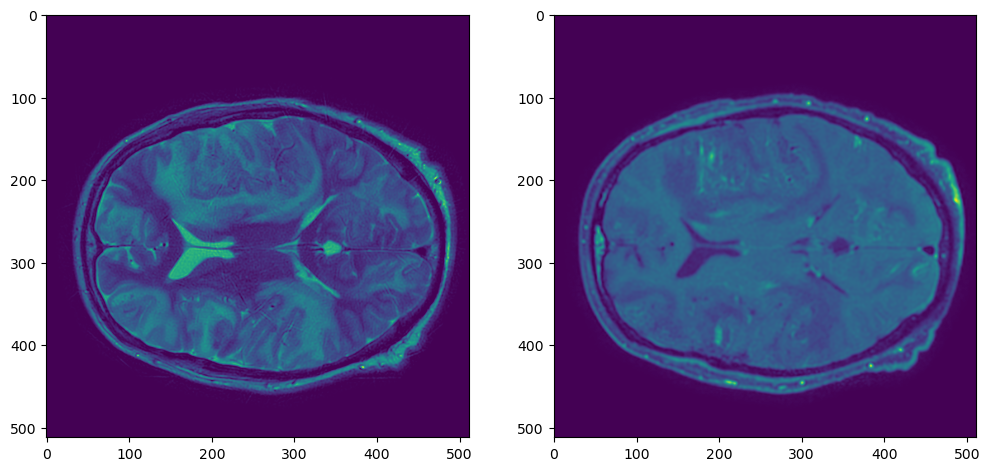
Работает довольно медленно, но есть решение быстрее.
2. Ресемплинг с SimpleITK 🔗
filenamesDICOM = reader.GetGDCMSeriesFileNames('T2')
reader.SetFileNames(filenamesDICOM)
t2_sitk = reader.Execute()
t2_sitk
>> <SimpleITK.SimpleITK.Image; proxy of <Swig Object of type 'std::vector< itk::simple::Image >::value_type *' at 0x000002CF0A1E1090> >
Объект SimpleITK.SimpleITK.Image библиотеки SimpleITK также содержит информацию об ориентации вокселей в реальном мире. Но она хранится не в одной удобной матрице аффинной трансформации, а по кусочкам.
t2_sitk.GetOrigin() # то же самое, что четвертый столбец, только с минусом
>> (-99.3905, -143.058, -60.64)
t2_sitk.GetSpacing() # то есть насколько далеко каждый отдельный воксель начинается относительно соседнего по каждой оси
>> (0.429688, 0.429688, 3.0000070292848084)
t2_sitk.GetDirection() # расплющенная косинусная матрица, задающая вращение воксельного облака относительно реального мира
>> (0.9826872663587349,
0.03894401075470161,
-0.18113282574601006,
-0.03040569918977931,
0.9983022756891978,
0.04967957136036232,
0.18276003390560375,
-0.04331201196096025,
0.9822030541729729)
В принципе, все то же самое можно достать и из матрицы аффинной трансформации. Ну например, зная, что каждый ее столбец влияет на одну координату вокселя, можно посчитать маштабирование (т.е. спейсинг, расстояние между началами вокселей). Это обычная евклидова норма.
x_scale = np.linalg.norm(t2_nib.affine[:,0])
y_scale = np.linalg.norm(t2_nib.affine[:,1])
z_scale = np.linalg.norm(t2_nib.affine[:,2])
print(x_scale, y_scale, z_scale)
>> 0.42968800290830866 0.4296879971521231 3.0000068992676026
Очевидно, если разделить каждый столбец на значение спейсинга, то получится косинусная матрица.
t2_pure_rotation = np.hstack((t2_nib.affine[:,0].reshape(-1,1)/x_scale,
t2_nib.affine[:,1].reshape(-1,1)/y_scale,
t2_nib.affine[:,2].reshape(-1,1)/z_scale,
t2_nib.affine[:,3].reshape(-1,1)))
t2_pure_rotation[:3,:3]
>> array([[-0.9827, -0.0389, 0.1811],
[ 0.0304, -0.9983, -0.0497],
[ 0.1828, -0.0433, 0.9822]])
Первые две строки отличаются по знаку от значений в косинусной матрице из SimpleITK. Не уверен, почему так происходит. Может, потому что подразумевается обратное направление координатной оси.
Кстати, эта информация может быть получена и напрямую из DICOM-файлов. Там есть специальный тег для этого.
cosine_from_dcm = pydicom.dcmread(filenamesDICOM[1]).ImageOrientationPatient
cosine_from_dcm
>> [0.982687, -0.030406, 0.182760, 0.038944, 0.998302, -0.043312]
Как видите, он хранит информацию только о двух строках (6 чисел вместо 9). Это ничего, ведь мы можем вычислить третью строку. Она перпендикулярна векторам первых двух строк, так что требуется просто посчитать их векторное произведение:
np.cross(cosine_from_dcm[:3], cosine_from_dcm[3:])
>> array([-0.1811, 0.0497, 0.9822])
Вернемся к ресемплингу. В SimpleITK он организован чуть сложнее, чем в nilearn, но все равно довольно самоочевиден.
def resample(image, ref_image):
resampler = sitk.ResampleImageFilter()
resampler.SetReferenceImage(ref_image)
resampler.SetInterpolator(sitk.sitkLinear)
resampler.SetTransform(sitk.AffineTransform(image.GetDimension()))
resampler.SetOutputSpacing(ref_image.GetSpacing())
resampler.SetSize(ref_image.GetSize())
resampler.SetOutputDirection(ref_image.GetDirection())
resampler.SetOutputOrigin(ref_image.GetOrigin())
resampler.SetDefaultPixelValue(image.GetPixelIDValue())
resamped_image = resampler.Execute(image)
return resamped_image
%%time
t1_resampled = resample(t1_sitk, t2_sitk)
t2_sitk_array = sitk.GetArrayFromImage(t2_sitk)
t1_resampled_array = sitk.GetArrayFromImage(t1_resampled)
plt.figure(figsize=(12,6))
plt.subplot(121)
plt.imshow(t2_sitk_array[t2_sitk_array.shape[0]//2,:,:])
plt.subplot(122)
plt.imshow(t1_resampled_array[t1_resampled_array.shape[0]//2,:,:])
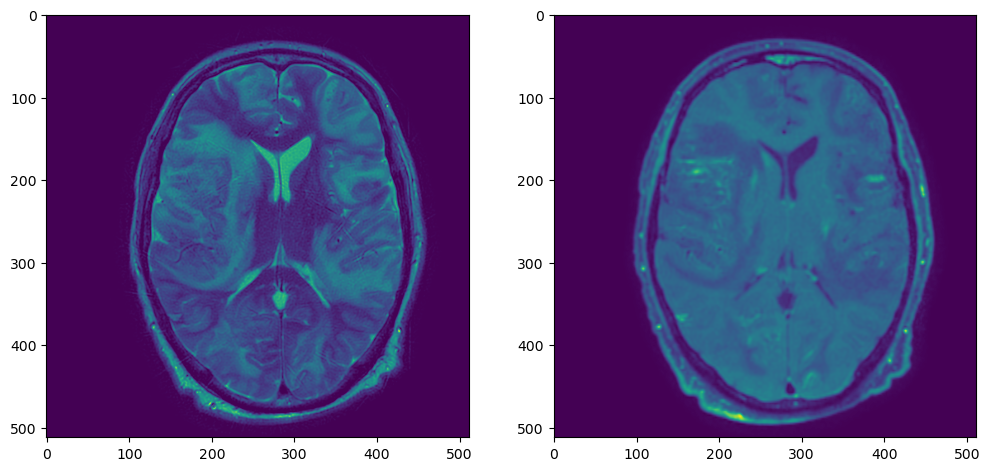
Работает гораздо быстрее:
def normalize(data):
return (data - np.min(data)) / (np.max(data) - np.min(data))
%%time
filenamesDICOM = reader.GetGDCMSeriesFileNames('T1_CE')
reader.SetFileNames(filenamesDICOM)
t1_sitk = reader.Execute()
filenamesDICOM = reader.GetGDCMSeriesFileNames('SWI')
reader.SetFileNames(filenamesDICOM)
swi_sitk = reader.Execute()
filenamesDICOM = reader.GetGDCMSeriesFileNames('T2')
reader.SetFileNames(filenamesDICOM)
t2_sitk = reader.Execute()
swi_resampled = resample(swi_sitk, t2_sitk)
t1_resampled = resample(t1_sitk, t2_sitk)
t2_sitk_array = normalize(sitk.GetArrayFromImage(t2_sitk))
swi_resampled_array = normalize(sitk.GetArrayFromImage(swi_resampled))
t1_resampled_array = normalize(sitk.GetArrayFromImage(t1_resampled))
stacked = np.stack([t2_sitk_array, swi_resampled_array, t1_resampled_array,])
to_rgb = stacked[:,t2_sitk_array.shape[0]//2,:,:].transpose(1,2,0)
im = Image.fromarray((to_rgb * 255).astype(np.uint8))
im
>>CPU times: total: 5.02 s
Wall time: 3.52 s